python 服务器批处理得到PSSM矩阵的问题
目录
- 1. 在linux上安装psiblast
- 2.下载并编译用于比对的大型蛋白质数据库
- 3. 获取PSSM矩阵
- 1)单条蛋白质序列的处理方法
- 2)批处理获取的方法
- 参考文献:
1. 在linux上安装psiblast
最好新建一个python环境,因为我发现conda安装blast默认的是python==3.6.11,可能会不小心把你的python版本改掉…然后你写好的代码全die了……
conda create -n blast python==3.6.11 source activate blast conda install -c bioconda blast
2.下载并编译用于比对的大型蛋白质数据库
nr和uniprot是比较通用的数据库:
ftp://ftp.ncbi.nlm.nih.gov/blast/db/
https://www.uniprot.org/downloads
1)nr是ncbi收集的目前所有微生物的蛋白序列,是用来计算氨基酸一般情况下的频率的,160G
2)uniprot90根据相似性做了一个去冗余,所以比nr要小很多,56G
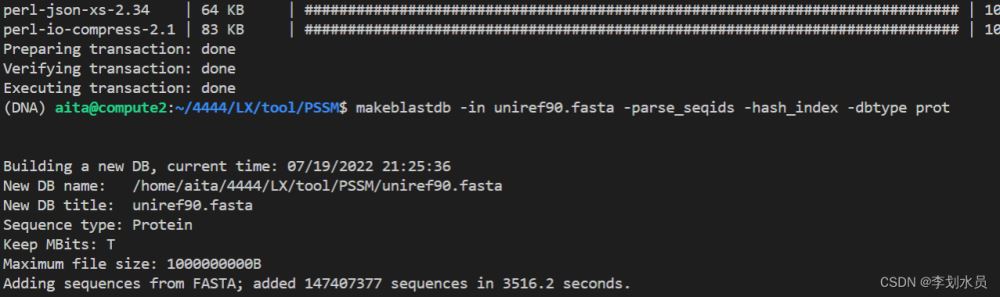
# 以uniprot90为例 wget ftp://ftp.uniprot.org/pub/databases/uniprot/uniref/uniref90/uniref90.fasta.gz # 下载 gzip -d uniref90.fasta.gz # 解压 makeblastdb -in uniref90.fasta -parse_seqids -hash_index -dbtype prot # 编译
解析完成后的样子:
文件是这个样子:(只截取了一部分)
3. 获取PSSM矩阵
我的初始文件是:
P00269.fasta是对单条蛋白质处理,里面的格式是:

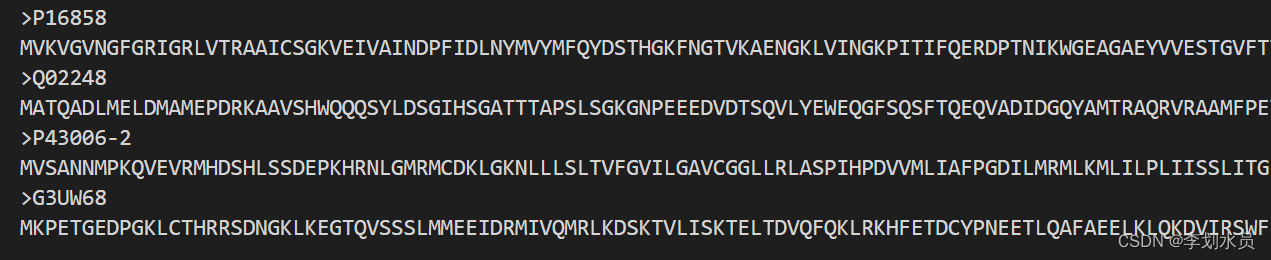
testset.fasta是对蛋白质集合批处理,里面的格式是(也可以单独蛋白质存为.fasta文件,由于blast只能处理单条蛋白糊,把这个集合知识归总的意思,第一步还是要生成单条蛋白质的.fasta文件,所以这个文件看个人意愿):
1)单条蛋白质序列的处理方法
import os
os.system('psiblast -query dataset/P00269.fasta -db /PSSM/uniref90.fasta -num_iterations 3 -out_ascii_pssm /dataset/P00269.pssm')##这个蛋白质好慢呀
2)批处理获取的方法
import os
file_name='/dataset/testset.fasta'
Protein_id=[]
with open(file_name,'r') as fp:
i=0
for line in fp:
if i%2==0:
# Protein_id.append(line[1:-1])
id=line[0:-1]
p=line[1:-1]
with open ('/dataset/'+str(p)+'.fasta','a') as protein:
protein.write(id)
# protein.write()
if i%2==1:
seq=line[0:-1]
with open ('/dataset/'+str(p)+'.fasta','a') as protein:
protein.write('\n')
protein.write(seq)
i=i+1
os.system('psiblast -query '+'/dataset/'+str(p)+'.fasta -db /PSSM/uniref90.fasta -num_iterations 3 -out_ascii_pssm /dataset/'+str(p)+'.pssm')
##PSSM真是太慢了,下面是只生成一个后的截图
emmmm,在研究怎么把这个矩阵存入文件方便调用,今天应该会更新……但是他好慢啊,不想用了。
参考文献:
到此这篇关于python服务器批处理得到PSSM矩阵的文章就介绍到这了,更多相关python服务器批处理内容请搜索我们以前的文章或继续浏览下面的相关文章希望大家以后多多支持我们!
赞 (0)

