R语言glmnet包lasso回归中分类变量的处理图文详解
我们在既往文章《手把手教你使用R语言做LASSO 回归》中介绍了glmnet包进行lasso回归,后台不少粉丝发信息向我问到分类变量处理的问题,我后面查了一下资料之前文章分类变量没有处理,非常抱歉。现在来重新聊一聊分类变量的处理。
我们导入glmnet包的时候可以看到,还需要导入一个Matrix包,说明这个矩阵包很重要

按照glmnet包的原文如下:

就是告诉我们,除了Cox Model外,其他的表达都支持矩阵形式,在Cox Model的介绍中,函数样式为


说明我们应该把其他变量变为矩阵的形式。这样说得不是很明白,下面我们来举个例子说明,继续使用我们的乳腺癌数据(公众号回复:乳腺癌,可以获得数据)我们先导入数据和R包
library(glmnet)
library(foreign)
library("survival")
bc <- read.spss("E:/r/Breast cancer survival agec.sav",
use.value.labels=F, to.data.frame=T)
bc <- na.omit(bc)
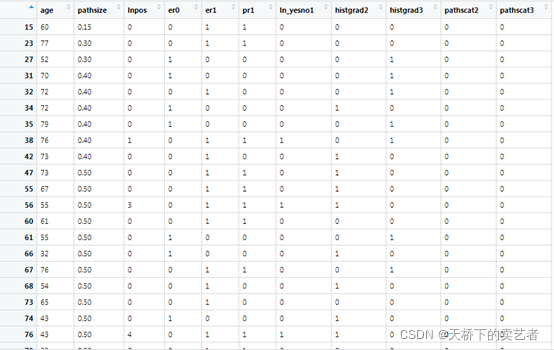
我们先来看看数据:
age表示年龄,pathsize表示病理肿瘤大小(厘米),lnpos表示腋窝淋巴结阳性,histgrad表示病理组织学等级,er表示雌激素受体状态,pr表示孕激素受体状态,status结局事件是否死亡,pathscat表示病理肿瘤大小类别(分组变量),ln_yesno表示是否有淋巴结肿大,time是生存时间,后面的agec是我们自己设定的,不用管它。

接下来删除缺失变量和把分类变量转成因子
bc$er<-as.factor(bc$er) bc$pr<-as.factor(bc$pr) bc$ln_yesno<-as.factor(bc$ln_yesno) bc$histgrad<-as.factor(bc$histgrad) bc$pathscat<-as.factor(bc$pathscat)
我们先来进行一个lasso的cox模型
glmnet包只能接受矩阵形式的数据,我们要分别进行转换
先把结局和时间提取出来
y<-bc$status time<-bc$time
把id,结局变量,时间变量和一个乱七八糟的变量删掉
data1<-bc[,-c(1,8,11,12)]##把id,结局变量,时间变量和一个乱七八糟的变量删掉
把分类变量变成哑变量矩阵形式
model_mat <-model.matrix(~ +er+pr+ln_yesno+histgrad+pathscat-1,data1)###把分类变量变成哑变量矩阵形式
重新组成数据,也就是我们需要的x
x<-as.matrix(data.frame(age=data1$age,
pathsize=data1$pathsize,lnpos=data1$lnpos,model_mat))#重新组合成数据
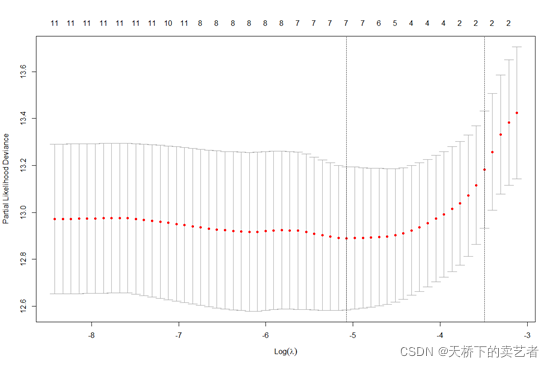
弄好x就可以进行分析了,交叉验证最好设一个种子,
set.seed(123) cv.fit <- cv.glmnet(x,Surv(time,y),family="cox", maxit = 1000) plot(cv.fit)
maxit = 1000是让它迭代100次的意思,如果迭代没到1000次,可能会出现一次报错,这在官方说明里面也有讲到,但我用两种方法算了一遍,结果都是一样的,没有错

下图是官方说明
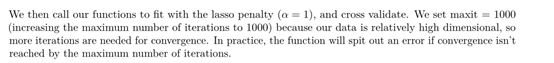
有兴趣的可以试一下这样算,结果也是一样的,但也要先设一个种子
set.seed(123) cv.fit1<- cv.glmnet(x,Surv(time,y),family="cox", alpha=1,nfolds=10) plot(cv.fit1)
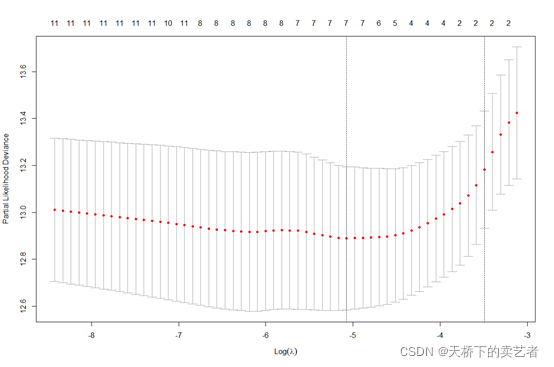
取最小值,也都是一样的
cv.fit$lambda.min cv.fit1$lambda.min

fit <- glmnet(x, Surv(time,y), family = "cox", maxit = 1000) plot(fit)
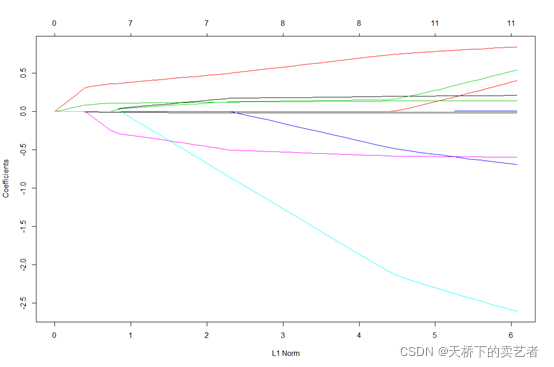
查看和提取系数
Coefficients <- coef(fit, s = cv.fit$lambda.min) Active.Index <- which(Coefficients != 0) Active.Coefficients <- Coefficients[Active.Index] Active.Index Active.Coefficients
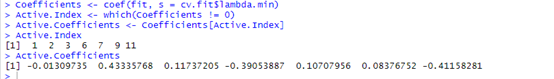
上图标出了最后还剩下的变量(指的是它的位置)和变量的系数,自己对照x看一下就可以了。值得一提的是我看到官方的示例cox模型只取最小的lambda,这样大家就不用这么纠结了,还有一个是它没有预测功能,不能进行预测。
下面来进行Binomial Models,也就是我们的二分类变量模型,其实就是不用时间变量就行了,其他都差不多,继续拿乳腺癌数据演示,懒得找数据了,上一篇文章就是拿乳腺癌来模拟二分类数据的(当时没找到好的数据)。
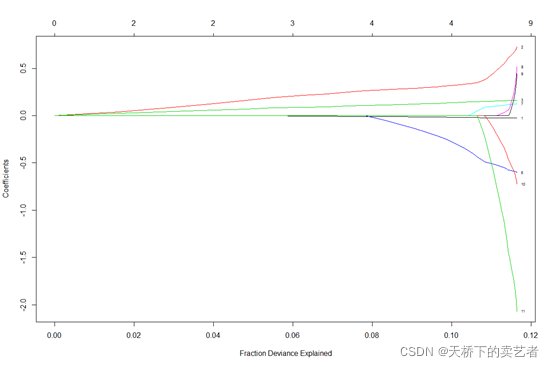
fit1 = glmnet(x, y, family = "binomial") plot(fit1, xvar = "dev", label = TRUE)
换成lambda
plot(fit1, xvar="lambda", label=TRUE)

其实到了这里基本和上一篇差不多了
set.seed(999) cvfit=cv.glmnet(x,y, family = "binomial") plot(cvfit)
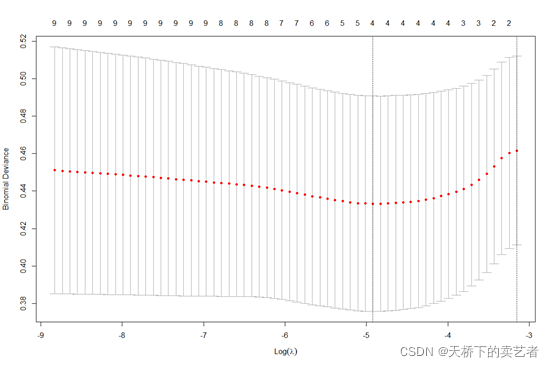
求出最小值
cvfit$lambda.min#求出最小值 cvfit$lambda.1se#求出最小值一个标准误的λ值

求出系数
coef1<-coef(cvfit, s = "lambda.min") coef2<-coef(cvfit, s = "lambda.1se") coef1 coef2
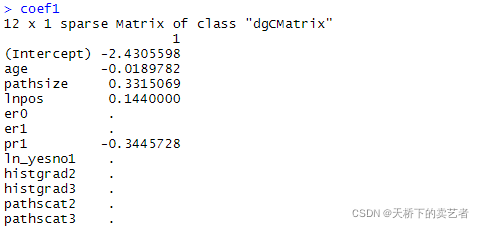
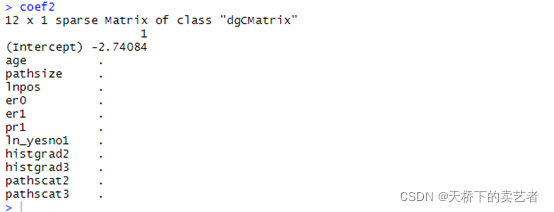
有一个已经被怼没有了,只能选coef1了。
到此这篇关于R语言glmnet包lasso回归中分类变量处理的文章就介绍到这了,更多相关R语言lasso回归分类变量内容请搜索我们以前的文章或继续浏览下面的相关文章希望大家以后多多支持我们!

